~2020年、琉球大学は開学70周年を迎えます。~
Island wisdom, for the world, for the future.
琉球大学のトーマ・クラウディア准教授、佐藤行人特命講師と、スリランカ・ペラデニヤ大学 (University of Peradeniya)のチャンディカ・ガマゲ(Chandika D. Gamage)博士らの国際研究チームによる成果が、米国の学術雑誌「PLOS Neglected Tropical Diseases」誌に掲載されます。
<発表のポイント>◆水中に存在する「環境DNA」を分析する手法で、人に感染症を起こす病原体レプトスピラを高感度で検出 |
<発表概要>
琉球大学大学院・医学研究科のトーマ・クラウディア・准教授、同大学・戦略的研究プロジェクトセンターの佐藤行人・特命講師、スリランカ・ペラデニヤ大学のチャンディカ・ガマゲ(Chandika D. Gamage)博士らは、哺乳類などの動物からヒトに伝搬して感染症を引き起こす病原体レプトスピラ(図1;注1)について、農業用の灌漑水から高感度でDNA検出できることを示しました。さらに、レプトスピラと同時に検出される動物のDNAを調べることで、家畜や野生動物を直接調査しなくても、レプトスピラの感染源となっている動物の候補(スイギュウ、ジャコウネコなど)が推定できることを示しました。
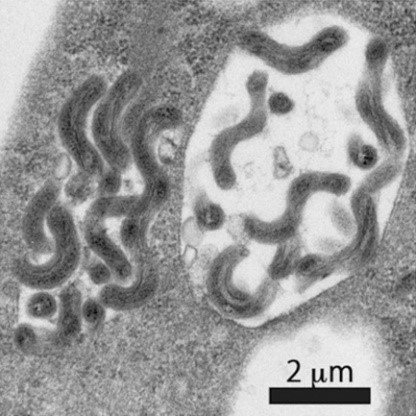
図1.細胞内に見られるレプトスピラ
レプトスピラは、ヒトや家畜を含む多くの哺乳類に感染して、高熱や黄疸、腎障害などを起こす人獣共通感染症(注2)の病原細菌です。レプトスピラを保菌する動物の尿から水や土壌が汚染されることでヒトに感染し、時には深刻な集団発生を起こします。このレプトスピラ症は、アフリカのエチオピアや中南米のブラジル、東南アジアのタイやインドネシアなど熱帯・亜熱帯地域で多く発生し、全世界では年間100万件以上の症例があり、6万人近くが亡くなっていると推定されています。その病原体であるレプトスピラは、汚染された水や土壌からでも単離・培養することが困難です。そのため、レプトスピラ症が流行する地域で、レプトスピラがどのような場所に多く潜んでいるのか、また、どのような動物がレプトスピラの感染源として注意するべきなのかを調べることは、容易ではありません。このことは、流行地において適切な予防方針を得る上での障壁となっています。
そこで本研究は、自然環境から単離・培養して調査することが難しいレプトスピラについて、環境DNA(注3)を分析するという手法に注目しました。この手法は、川や海などの水に懸濁物として含まれる微量なDNAを抽出して、そのDNAの配列情報を大規模に解析することにより、微生物や、排泄物・毛・粘液などを排出している動物の存在を高感度で分析することができます(図2)。トーマ准教授と佐藤講師らは、この環境DNAを活用したレプトスピラの分析手法をすでに開発し、沖縄県内の流行地で成果を挙げています(注4)。今回、琉球大学の外国人客員研究員として訪日したガマゲ博士と共同で、開発した手法をスリランカにおけるレプトスピラ流行地の分析へと応用しました。
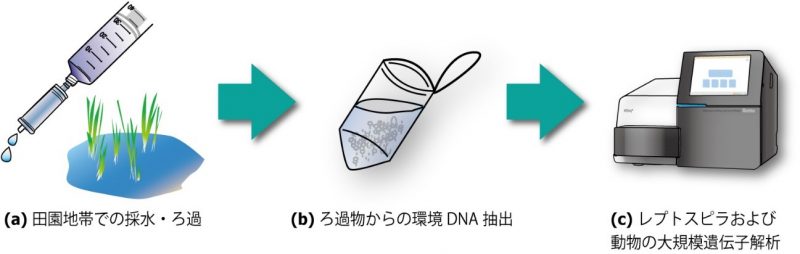
図2.環境DNAによるレプトスピラ分析法の概要.
(a) 500 mL の環境水を採取・ろ過して懸濁物を濃縮.(b) フィルターユニットから専用の器具と試薬を用いてDNAを抽出、レプトスピラが保有する16S rRNAとflaB遺伝子(注5,6)、動物のミトコンドリアDNAが保有する12S rRNA遺伝子(注7)をターゲットとしたPCR (注8)を行う.(c) 増幅したDNAを次世代シークエンサー(注9)とスーパーコンピューターで大規模解析し、各配列が由来する生物(レプトスピラ、動物、他の細菌類など)を推定、配列数を測定する
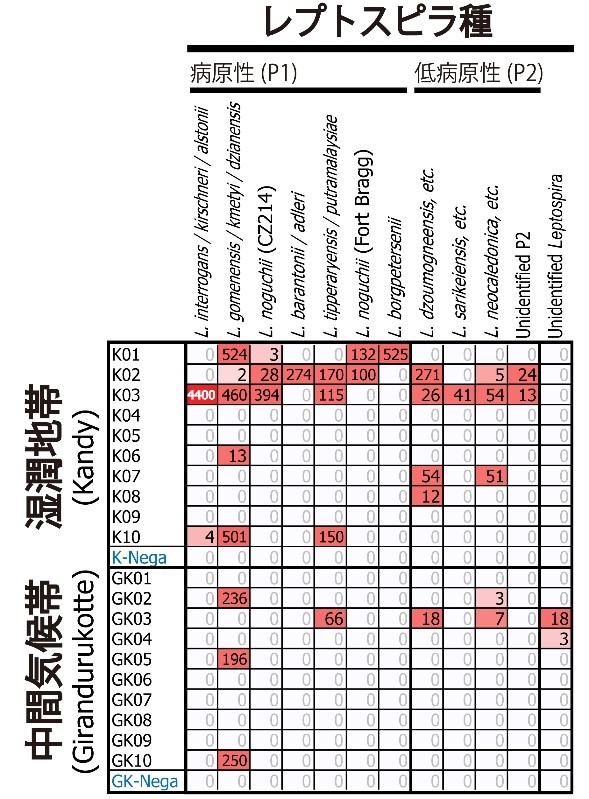
その結果、スリランカの中で湿潤な気候帯を代表する地域キャンディ(Kandy)近郊の灌漑水では、ヒトに対して強い病原性を示すレプトスピラの種 Leptospira interrogans とL. noguchiiが検出されました(図3)。低病原性や配列未報告の種を含めると11種以上の多様なレプトスピラが、多数(数千配列)検出されています。一方、中間的な気候帯のギランドゥルコッテ(Giradurukotte)では、レプトスピラ配列の強い検出は見られず、病原性の2種程度とその他の3種程度が、数百配列検出されたのみでした(図3)。
図3.スリランカの代表的な農業-気候地帯におけるレプトスピラの環境DNA検出.
列(縦)は検出されたレプトスピラの種類を表し、行(横)は各採水サンプル(地域あたり10個ずつ)を表す.色が濃いほど、多数のレプトスピラDNA配列が検出されたことを表す.DNA配列の数は、環境水が含むレプトスピラの菌数におよそ比例する数値であるが、測定誤差を含んだ半定量的なものであり、菌数そのものではない.当該論文Gamage et al. (2020)に基づき作成
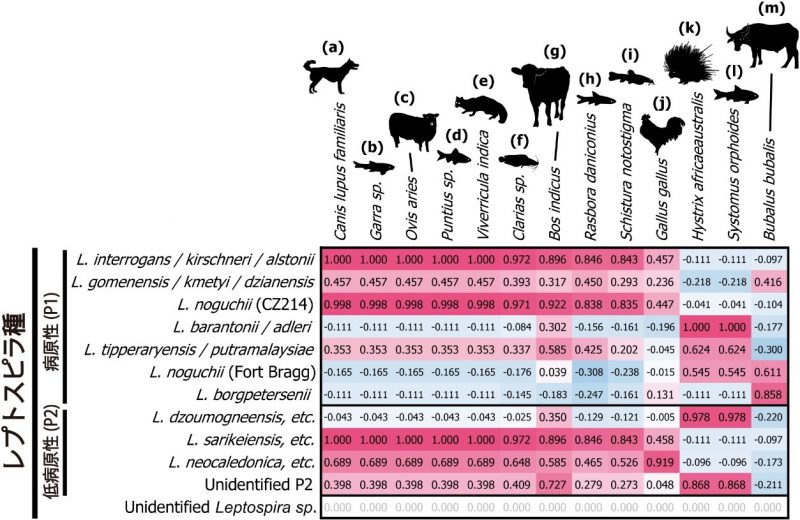
さらに、同じ環境DNAサンプルから動物のDNAを分析したところ、湿潤地帯であるキャンディ(Kandy)近郊の灌漑水では、イヌ、ヒツジ(または近縁種)、ジャコウネコ、ウシ、ニワトリ、タテガミヤマアラシ、スイギュウが、レプトスピラ(いずれかの種)と同時に検出されることが分かりました(図4)。これらの動物のうちニワトリ以外では、レプトスピラの抗体を持った保菌動物であるという報告が、他の国や地域で行われた過去の研究から確認できました。今回スリランカで検出された動物の多くは、レプトスピラ症に関する知見が少ないスリランカの当該地域においても、レプトスピラの重要な感染源である可能性が指摘されます。ただし、検出された動物の中には、淡水魚などレプトスピラとの関係が不明瞭なものも含まれています。それらは保菌動物ではなく、灌漑水にもともと生息することから、偶然、相関が検出されたに過ぎない可能性があります。なお、中間的な気候帯のギランドゥルコッテ(Giradurukotte)では、レプトスピラと相関する哺乳類や鳥類は検出されませんでした。
図4.湿潤地帯キャンディ(Kandy)でレプトスピラと有意に相関して検出された動物種.
列(縦)は動物の種を表し、行(横)はレプトスピラの種を表す.赤色が濃いほど、該当する動物種とレプトスピラ種の検出DNA配列数間の相関係数(r)が高いこと示す.値が 0.79以上だと統計的に有意(Benjamini-Hochberg法による多重比較検定補正後の有意水準1%). (a)イヌ、(b)コイ科ガラ属淡水魚、(c)ヒツジまたはヤギ亜科近縁種、(d)コイ科プンティウス属淡水魚、(e)コジャコウネコ、(f)ヒレナマズ科Clarias属淡水魚、(g)ウシ、(h)コイ科ラスボラ属淡水魚、(i)フクドジョウ科スキストゥラ属淡水魚、(j)ニワトリ、(k)タテガミヤマアラシ近縁種、(l)コイ科Systomus属淡水魚、(m)アジアスイギュウ.当該論文Gamage et al. (2020)に基づき作成
本研究は、同様の手法で細菌類全般を対象としたDNA分析も行っており、レプトスピラと同時に出現する22種の細菌を報告しています(キャンディ近郊の灌漑水から16種、ギランドゥルコッテ近郊の灌漑水から6種;図5)。その中には、ウシの流産やヒトの敗血症と腸炎、食用鶏肉の汚染との関連性が報告されているArcobacter cryaerophilus が含まれました。レプトスピラと他の病原細菌との相互作用も関係した環境衛生上の課題が提起されます。
図5.本研究の調査地となった水田・圃場地帯の風景例.
(a)キャンディ(Kandy)および(b)ギランドゥルコッテ(Giradurukotte).前者では棚田、後者では平地の水田が主であり、一部ではスイギュウを用いた伝統的な牛耕が行われている.当該論文Gamage et al. (2020)に基づき作成
以上の研究結果より、トーマ准教授と佐藤講師らが取り組んできたレプトスピラの環境DNA分析法は、家畜・野生動物の抗体調査といった大規模な疫学調査が困難なレプトスピラ症流行地において、レプトスピラの危険因子(レプトスピラの存在場所や感染源の候補動物)を推定する調査手法として極めて有用であることが示されました。今回の研究で得たような環境DNA分析の結果に基づけば、より効率的に、レプトスピラの単離・培養を目指すピンポイントな環境調査や、対象動物を絞った抗体検査と感染源の特定など、実証的な研究に進むことが出来ます。それらによって、世界のとくに亜熱帯・熱帯域に属する様々な国や地域で、レプトスピラ症の環境リスク評価、保菌動物の管理、衛生環境の改善、予防指針の策定などが進むと期待されます。このように、人・動物・環境の関係を理解して感染症対策や防疫に取り組む視点はOne Healthアプローチと呼ばれ、近年注目が高まっています。本研究は、環境DNA技術をOne Healthへ応用した試みとも言えます。
レプトスピラ研究のさらなる展開としては、環境中でのレプトスピラの生存に寄与しており、現在も未知のままである共生微生物(細菌、真菌、単細胞真核生物など)の探索が挙げられるかもしれません。それらレプトスピラの共生微生物も、今回行ったような環境DNAの相関から推定できる可能性があり、基礎生物学上も疫学上も重要な課題です。そして、今回得たレプトスピラ流行地の環境DNAサンプルは、レプトスピラの生態を反映・記録した貴重な環境DNAバイオバンクサンプルとして、こうした次の研究の展開にも活用できます。本研究は、琉球大学の複数の部局とスリランカ・ペラデニヤ大学の研究者によって行われたもので、細菌学、獣医学、疫学、遺伝学、生命情報科学、生態学など、様々な分野の専門知識と技術を持った研究者が共同研究することにより実現しました。
<用語解説>
(注1)レプトスピラ: らせん形の細長い細菌。64種ほどが知られており、病原性・低病原性・非病原性に分けられる。病原性と低病原性の種は、人獣共通感染症のレプトスピラ症を起こす。
(注2)人獣共通感染症: ヒトと動物(哺乳類・鳥類など)に、共通して感染する病原体によって発症する疾患(病気)のこと。病原体となるものは、インフルエンザウィルスなどのほか細菌、真菌、原虫、寄生虫など多岐に渡る。
(注3)環境DNA: 河川水や土壌などの環境媒質中に微量に含まれる生物由来のDNA断片。主な由来は、付近に生息する生物の皮膚片や羽毛、粘液、細胞片、死骸などであると考えられている。
(注4)琉球大学・新潟大学・神戸大学2019年4月25日共同ニュースリリース: 「川の水から人獣共通感染症の病原体と保菌動物の候補を同時検出 ~レプトスピラ症予防に向けた環境DNA分析手法を開発~」https://www.u-ryukyu.ac.jp/news/4788/
(注5)16S rRNA: タンパク質の生成に関わるリボソームRNAの一部をコードする遺伝子。バクテリアなどの原核生物に広く共通する遺伝子であるため、その種判別に多用される。
(注6)FlaB: 細菌の鞭毛を構成するタンパク質をコードする遺伝子。病原性レプトスピラの高特異度検出に使用される。
(注7)12S rRNA: タンパク質の生成に関わるリボソームRNAの一部をコードする遺伝子。ミトコンドリアゲノムに存在し、脊椎動物など多細胞動物に広く共通する遺伝子であるため、その種判別に利用される。
(注8)PCR: ポリメラーゼ連鎖反応の略。DNAの集合から、ターゲットとする特定の配列に挟まれた領域を生化学的に増幅する方法。ごく微量の環境DNAサンプルから、多数のコピーDNAを得て、DNA配列決定などの分析に使用することができる。
(注9)次世代シークエンサー: 数千万から数億分子のDNAについて、同時並列的に塩基配列を解読することができる機器。2004年ごろから普及し、生物学で使われる重要技術の1つになっている。
<謝辞>
本研究は、次の研究助成のもとで行われました:文部科学省・科学研究費補助金(17K19298、18H02655、20K12258)、琉球大学・時空間ゲノミクスプロジェクト、および同大学・外国人客員研究員制度。ならびに、同大学・研究基盤センターと戦略的研究プロジェクトセンターによる共同利用・共同研究の支援を受けました。また、情報・システム研究機構・国立遺伝学研究所が有する遺伝研スーパーコンピュータシステムを利用しました。
<論文情報>
論文タイトル:Understanding leptospirosis eco-epidemiology by environmental DNA metabarcoding of irrigation water from two agro-ecological regions of Sri Lanka
(和訳)スリランカにおける2種類の農業生態地域で実施した潅漑水の環境DNAメタバーコーディング分析によるレプトスピラ症の生態疫学的理解
雑誌名: PLOS Neglected Tropical Diseases
著 者: Chandika D. Gamage, Yukuto Sato, Ryosuke Kimura, Tetsu Yamashiro, Claudia Toma
チャンディカ・ガマゲ(ペラデニヤ大 医学部 部門長上級講師)、佐藤行人(琉球大 戦略的研究プロジェクトセンター 特命講師)、木村亮介(琉球大院 医学研究科 准教授)、山城哲(琉球大院 医学研究科 教授)、トーマ・クラウディア(琉球大院 医学研究科 准教授)
DOI番号: 10.1371/journal.pntd.0008437
URL: https://journals.plos.org/plosntds/article?id=10.1371/journal.pntd.0008437